Abstract
Phylogeographic and morphometric evidence can be used to cluster Apis mellifera subspecies into evolutionary lineages or branches. Mitochondrial DNA sequence and restriction site analyses have shown similar clustering of subspecies groups. Thus, mtDNA variation can be used to infer honey bee evolutionary relationships. In this paper, we describe three 16S mtDNA PCR-RFLP patterns, each one completely associated with a previously determined A, M, or C Dra I restriction pattern of the COI-COII region. These results indicate that the COI-COII and the 16S genes have had a very closely linked evolutionary history. Although distinct patterns were obtained with Eco RI, Alu I, Hinc II and Taq I, the best differentiation among the three patterns was observed with Dra I and Vsp I enzymes. Nucleotide sequence analysis of the16S gene fragment displayed 10 sites of base substitution (1.35%) among the three patterns and two insertions in the A. m. scutellata pattern.
Zusammenfassung
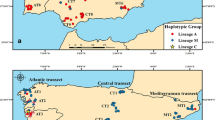
Ähnlich wie phylogeographische und morphometrische Evidenzen können auch Daten zu Variationen in der mitochondrialen DNA (mtDNA) herangezogen werden, um Schlüsse hinsichtlich evolutiver Beziehungen zu ziehen. Der Verdau der mitochondrialen intergenen COI-COII Region mittels DraI (Garnery et al., 1993) stellt gegenwärtig die Methode mit der besten Auflösung für die Charakterisierung und Zuordnung von Subspezies zu mitochondialen Linien dar. Populationsanalysen mittels mtDNA-Polymorphismen können dementsprechend ein wertvolles Werkzeug darstellen, um Richtungen und Mechanismen in der mtDNA-Genomevolution zu untersuchen. Als Teil einer Suche nach neuer mtDNA Variabilität beschreibt diese Studie die Amplifikations- und Restriktionsmuster für eine weitere mitochondriale DNA Region (16S) in Proben, die zuvor hinsichtlich ihrer COI-COII-Muster als A, M oder C klassifiziert wurden. Insgesamt wurden Proben von 38 Völkern mit M-Muster, 89 mit dem C- und 232 mit dem A-Muster gewonnen. Die Orte der Probennahmen und die jeweilige Zahl der untersuchten Völkern sind in Tabelle I zusammengestellt. DNA wurde individuell mittels Phenol-Chloroform aus Thoraxstücken extrahiert. Die DNA-Fraktion wurde für die PCR-Amplifizierung des 16S Locus verwendet und anschliessend mittels der folgenden Enzyme verdaut: Hinc II, Vsp I, Alu I, Taq I, Eco RI und Dra I.Die amplifizierten Fragmente und die Produkte der Endonukleasenverdaue wurden in 8 %, bzw. 10 % Polyacrylamidgelen aufgetrennt. Restriktionsanalysen der mitochondrialen DNA der Cytochrom b (Bgl II), COI (Hinc II) und COI-COII (Dra I) Regionen wurden für eine vergleichende molekulare Charakterisierung der Honigbienenproben durchgeführt. Anhand der 16S Amplifizierung und der Restriktionsanalyse wurden drei Muster festgestellt, die entsprechend ihrer assoziierten COI-COII-Muster als A, M und C bezeichnet wurden (Abb. 2). Das amplifizierte 16S-Genfragment wies in den C- und M-Proben eine Grösse von 740 bp und in den A-Proben eine Grösse von 742 bp auf. Paarweise oder multiple Vergleiche der DNA-Sequenzen zeigten Nukleotidsubstitutionen an 10 Positionen (1,35 %) (Abb. 1). Das gemeinsame Vorkommen der M- und A-Muster in Spanien belegt die Ergebnisse früherer Studien und weist darauf hin, dass dieses Land eine sekundäre Kotaktzone zwischen diesen beiden Linien darstellt. In der vorliegenden Studie zeigten 17 von 44 Völkern aus Italien das M-Muster und eines das A-Muster. Dieses Ergebnis bestätigt frühere Analysen, die zeigten, dass italienische Honigbienenpopulationen aus den M- und C-Linien der mitochondrialen DNA zusammengesetzt sind. Obwohl mittels Eco RI, Alu I, Hinc II und Taq I-Verdau gut unterscheidbare Muster erzeugt werden konnten, war die klarste Differenzierung für die drei Haplotypen bei Dra I und VspI I-Verdauen zu beobachten. Die 16S mtDNA Variation kann nicht nur eine alternative Methode für die Identifizierung der maternalen DNA-Abstammung eines Volkes darstellen, vielmehr kann der in dieser Arbeit aufgezeigte Polymorphismus, zusammen mit anderen Polymorphismen, sich auch als nützlich erweisen, um Ereignisse der mtDNA-Evolution bei A. mellifera zu untersuchen
Similar content being viewed by others
References
Arias M.C., Sheppard W.S. (1996) Molecular phylogenetics of honey bee subspecies (Apis mellifera L.) inferred from mitochondrial DNA sequence, Mol. Phylogenet. Evol. 5, 557–566.
Avise J.C. (2000) Phylogeography: The history and formation of species, Harvard University Press, Cambridge, USA.
Cameron S.A. (1993) Multiple origins of advanced eusociality in bees inferred from mitochondrial DNA sequences, Proc. Natl Acad. Sci. 90, 8687–8691.
Clarke K.E., Oldroyd B.P., Quezada-Euán J.J.G., Rinderer T.E. (2001) Origin of honeybees (Apis mellifera) from the Yucatan peninsula inferred from mitochondrial DNA analysis, Mol. Ecol. 10, 1347–1355.
Collet T. (2004) Estrutura genética das populações de abelhas africanizadas (Apis mellifera L.) do Brasil e Uruguai determinada por meio de polimorfismos do DNA mitocondrial, MSc Thesis, Universidade Federal de São Carlos, SP, Brazil, 66 p.
Crozier R.H., Crozier Y.C. (1993) The mitochondrial genome of the honeybee Apis mellifera: complete sequence and genome organization, Genetics 133, 97–117.
Crozier Y.C., Koulianos S., Crozier R.H. (1991) An improved test for Africanized honey bee mitochondrial DNA, Experientia 47, 968–969.
de la Rúa P., Galián J., Serrano J., Moritz R.F.A. (2001a) Molecular characterization and population structure of the honeybees from the Balearic islands (Spain), Apidologie 32, 417–427.
de la Rúa P., Galián J., Serrano J., Moritz R.F.A. (2001b) Genetic structure and distinctness of Apis mellifera L. populations from the Canary Islands, Mol. Ecol. 10, 1733–1742.
Del Lama M.A., Lobo J.A., Soares A.E.E., Del Lama S.N. (1990) Genetic differentiation estimated by isozymic analysis of Africanized honeybee populations from Brazil and from Central America, Apidologie 21, 271–280.
Del Lama M.A., Souza R.O., Duran X.A., Soares A.E. (2004) Clinal variation and selection on MDH allozymes in honeybees in Chile, Hereditas 140, 149–53.
Diniz N.M., Soares A.E.E., Sheppard W.S., Del Lama M.A. (2003) Genetic structure of honeybee populations from southern Brazil and Uruguay, Genet. Mol. Biol. 26, 47–52.
Ferreira K.M. (2002) O padrão africano do DNA mitocondrial das abelhas africanizadas do Brasil tem origem diversa de Apis mellifera scutellata? MSc Thesis, Universidade Federal de São Carlos, SP, Brazil, 84 p.
Franck P., Garnery L., Solignac M., Cornuet J.M. (1998) The origin of west European subspecies of honeybees (Apis mellifera): new insights from microsatellite and mitochondrial data, Evolution 52, 1119–1134.
Franck P., Garnery L., Celebrano G., Solignac M., Cornuet J.M. (2000a) Hybrid origins of honeybees from Italy (Apis mellifera ligustica) and Sicily (A. m. sicula), Mol. Ecol. 9, 907–921.
Franck P., Garnery L., Solignac M., Cornuet J.M. (2000b) Molecular confirmation of a fourth lineage in honey bees from the Near East, Apidologie 31, 167–180.
Franck P., Garnery L., Loiseau A., Oldroyd B.P., Hepburn H.R., Solignac M., Cornuet J.M. (2001) Genetic diversity of the honeybee in Africa: microsatellite and mitochondrial data, Heredity 86, 420–430.
Garnery L., Cornuet J.M., Solignac M. (1992) Evolutionary history of the honey bee Apis mellifera inferred from mitochondrial DNA analysis, Mol. Ecol. 1, 145–154.
Garnery L., Solignac M., Celebrano G., Cornuet J.M. (1993) A simple test using restricted PCRamplified mitochondrial DNA to study the genetic structure of Apis mellifera L., Experientia 49, 1016–1020.
Garnery L., Mosshine E.H., Cornuet J.M. (1995) Mitochondrial DNA variation in Moroccan and Spanish honey bee populations, Mol. Ecol. 4, 465–471.
Gray M.W., Burger G., Lang B.F. (1999) Mitochondrial Evolution, Science 283, 1476–1481.
Hall H.G., Smith D.R. (1991) Distinguishing African and European honeybee matrilines using amplified mitochondrial DNA, Proc. Natl. Acad. Sci. (USA) 88, 4548–4552.
Lobo J.A., Del Lama M.A., Mestriner M.A. (1989) Population differentiation and racial admixture in the Africanized honeybee (Apis mellifera L.), Evolution 43, 794–802.
Moritz R.F.A., Cornuet J.M., Kryger P., Garnery L., Hepburn H.R. (1994) Mitochondrial DNA variability in South African honey bees (Apis mellifera L.), Apidologie 25, 169–178.
Oldroyd B.P., Cornuet J.M., Rowe D., Rinderer T.E., Crozier R.H. (1995) Racial admixture of Apis mellifera in Tasmania, Australia: similarities and differences with natural hybrid zones in Europe, Heredity 74, 315–325.
Prada C.F.Q. (2004) Estrutura genética das populações de abelhas africanizadas (Apis mellifera L.) da Colômbia estimada através de marcadores nucleares e mitocondriais, MSc Thesis, Universidade Federal de São Carlos, SP, Brazil, 96 p.
Quezada-Euán J.J.G., Pérez-Castro E.E., May-Itzá W. (2003) Hybridization between European and African-derived honeybee populations (Apis mellifera) at different altitudes in Peru, Apidologie 34, 217–225.
Ruttner F. (1988) Biogeography and taxonomy of honeybee, Springer-Verlag, Berlin, Heidelberg.
Ruttner F., Tassencourt I., Louveaux J. (1978) Biometrical-statistical analysis of the geographic variability of Apis mellifera L., Apidologie 9, 363–381.
Sheppard W.S., McPheron B.A. (1991) Ribosomal DNA diversity in Apidae, in: Smith D.R. (Ed.), Diversity of the genus Apis, Westview, Boulder, CO, pp. 89–102.
Sheppard W.S., Rinderer T.E., Mazolli J.A., Stelzer J.A., Shimanuki H. (1991) Gene flow between African- and European — derived honeybee populations in Argentina, Nature 349, 7882–7884.
Sheppard W.S., Arias M.C., Meixner M.D., Grech A. (1997) Apis mellifera ruttneri, a new honey bee subspecies from Malta, Apidologie 28, 287–293.
Smith D.R., Palopoli M.E, Taylor O.R., Garnery L., Cornuet J.M., Solignac M., Brown W.M. (1991) Geographical overlap of two mitochondrial genomes in Spanish honeybees (Apis mellifera iberica), J. Hered. 82, 96–100.
Souza R.O. (2002) Dinâmica do fluxo gênico em populações de Apis mellifera do Chile observada através de marcadores nucleares e mitocondriais, MSc Thesis, Universidade Federal de São Carlos, SP, Brazil, 87 p.
Whitfield J.B., Cameron S.A. (1998) Hierarchical analysis of variation in the mitochondrial 16S rRNA gene among Hymenoptera, Mol. Biol. Evol. 15, 1728–1743.
Author information
Authors and Affiliations
Corresponding author
Additional information
Manuscript editor: Klaus Hartfelder
Rights and permissions
About this article
Cite this article
Collet, T., Arias, M.C. & Del Lama, M.A. 16S mtDNA variation in Apis mellifera detected by PCR-RFLP. Apidologie 38, 47–54 (2007). https://doi.org/10.1051/apido:2006056
Received:
Accepted:
Issue Date:
DOI: https://doi.org/10.1051/apido:2006056